今回は「オンラインで3Dの化学を遊ぶ」と題して、オンラインで使用できる3D構造式エディタ「MolView」をご紹介します!
§ 分子の表し方
まずは、分子を理解する上で欠かせない「構造式」から復習していきましょう。
化学を履修したことのある皆さんは、有機化学の授業で構造式というものを習ったと思います。ここではプロピオン酸(分子式:$\mathrm{C_3 H_6 O_2}$)を例にとってみましょう。構造式とは次のようなものです。
構造式の書き方には色々と流儀があり、$$\mathrm{CH_3 CH_2 COOH}$$とだけ書くタイプ(これを「簡略構造式」と言います)や部分的に価標(元素記号を結んだ線のこと)を書くタイプ($\mathrm{CH_3 \text{-}CH_2\text{-}COOH}$)などの他、化学の専門書や大学の講義などでは元素記号まで省略して
とか、
などと表記することがあります。②や③の表記法は初見だと自分で描いたり理解したりするのが難しいかもしれませんが、何せ水素をいちいち描く必要が無いので慣れれば非常にラクです。ただし、構造式③の場合は構造式というよりも示性式と言った方がよいでしょう。
・・・とは言ったものの、皆さんは示性式と構造式の違いがちゃんと説明できますか?よく分からないという方のために簡単に説明しておきますと、構造式が価標によって全ての原子の結合を表した式であるのに対し、示性式とはその化合物の性質を分かりやすく伝えるために官能基を明示しただけの式を指しています。
例)構造式:$\mathrm{CH_3 \text{-}CH_2\text{-}COOH}$
示性式:$\mathrm{C_2 H_5 COOH}$
ただ、今回は示性式と構造式の違いについてあまり深く拘る必要がないので、このくらいでサラッと流します。
§ 構造式は万能ではない
さて、構造式は有機化学を学ぶ上で非常に重要なツールですが、一つ重大な欠点があります。それは
「分子の立体構造を正しく表すことができない」
という点です。例えばシクロヘキサンの場合、構造式は次のようになります。
これだけだとただの正六角形に見えるため、一見すると平べったいように思えますが、実はそうではありません。確かにシクロヘキサンを紙面の上側から見下ろせば平面構造に見えます(図5)が、実際には「椅子型」と呼ばれる、少し起伏のある構造をもっています(図6)。
※灰色の球は炭素、白色の球は水素を表しています。
§ MolViewで分子模型を作ってみよう
このように、構造式を勉強するだけでは有機化学のリアリティが理解しにくく、物性や反応論を学ぶ際にイメージが湧きにくいという側面もあります。そこで今回、皆さんにご紹介するのが「MolView」という無料ソフトです。何とこのMolView、オンラインでの利用が可能でダウンロードが不要なのです。そのため、スマホやタブレット端末でも簡単に利用できるところがポイントです(だからといって化学の授業中にやるのはあまりオススメしませんが(笑))。
使い方は非常にシンプルで、ウェブページ http://molview.org(外部リンク)にアクセスすると次のような画面が現れます。
デモンストレーションとして初期画面にカフェインの例が出ていますが、左上のゴミ箱ボタンを押せば画面をまっさらにすることができます。ここに各自好きな分子を描いてみましょう。
先ほどの例で取り上げたシクロヘキサンを描いてみると以下のようになります。
上のバーの「2D to 3D」というボタンを押すと、右側の黒い部分に分子の立体モデルが出力されます。この立体モデルはドラッグによって自由に回転させることができるので立体構造を把握する上で非常に有用です。
「2D to 3D」というボタンの隣に箒の形をしたボタンがありますが、これをクリックすると適当な見やすい形の構造式に描き直してくれます(「クリーン機能」といいます)。
また、元素記号の表示ON/OFFや、元素別のカラーリングもできますし、酸素や窒素などのヘテロ原子のほか、金属元素なども書き加えることができます。
これらの操作のみで、高校化学の教科書に載っている化合物ならほとんど全て再現可能です。以下に数例を示しておきます。
§ MolViewで化合物を理解する
MolViewではこうした立体モデルをもとにして、物質の結合長や結合角を求めることができます。ここではシクロヘキサン、ベンゼン、trans-2-ブタンを例に見てみます。なぜこの3つなのかについては特に説明不要な気がしますが、念のため解説しておきましょう。
炭素間結合における結合距離は炭素原子の混成状態に依存します。詳しい内容は割愛しますが、$\text{sp}^3$混成軌道の炭素間結合距離は実測値が約$0.154 \text{nm}$(cf.エタンの値)であり、$\text{sp}^2$混成軌道の炭素間結合距離の実測値は約$0.133 \text{nm}$(cf.エチレンの値)となっています。混成軌道におけるs軌道の占める割合を軌道の「s性」などといい、s性が大きいほど混成軌道は丸みを帯び、原子核間距離が短くなります。この辺りの感覚は、結合次数が増えるにしたがって結合が強固になるために結合距離が短くなる、という程度のものでも構いません。
単純な結合様式の場合、ほとんどの化合物でエタン(単結合)やエチレン(二重結合)、アセチレン(三重結合)と似たような結合距離を有するのですが、芳香族の場合は少し結合距離が変わってきます。ベンゼン環の炭素原子はいずれも等価であるために炭素間結合もまた全て等価であり、炭素間結合の結合次数は$1$や$2$という整数値でキッパリ分かれている訳ではありません。大学の教養化学で共鳴という概念を学ぶと思いますが、ベンゼン環の炭素間結合は言わば$1.5$重結合のようなもので、通常の単結合よりも距離が短く、二重結合よりも距離が少し長いという性質を持っています。ベンゼン環の炭素間結合距離の実測値は約$0.140 \text{nm}$となっており、確かにエタンの$0.154 \text{nm}$とエチレンの$0.133 \text{nm}$の間にありますよね?
そこでMolViewが実際の結合距離をどの程度再現しているかを調べるためにシクロヘキサン、ベンゼン、trans-2-ブタンの3つを例に取った、というわけです。以下にこれらの3Dモデルを示します。
これらを見て分かる通り、シクロヘキサンの$\sigma$結合は$0.153 \text{nm}$、ベンゼンの$\mathrm{C\text{-}C}$間結合は$0.139 \text{nm}$、trans-2-ブタンの$\pi$結合は$0.134\text{nm}$となっており、実測値がほぼ正確に反映されていますから、MolViewのプログラム内では実際の値にかなり即した形で分子のモデリングが行われていることが分かります。
そしてこのソフトウェアの凄いところは3Dモデルだけでなく電子密度や結合の極性、双極子モーメントが3Dで簡単に表示できるという点です。
一番上のバーに「Jmol」というメニューがあります。そこから「CALCULATIONS」の項の「MEP Surface lucent」を選んでください。すると次のような3Dモデルが得られます。ここでは例としてプロピオン酸の電子密度を示します。
どうでしょうか?皆さん上手く表示できたでしょうか?
図中の赤い部分が電子密度の高いところで、青くなるにしたがって電子密度が低下していきます。電気陰性度の大きい酸素原子のまわりが赤くなっており、酸素に電子を求引された部分は青くなっています。プロピオン酸の場合はカルボキシ基が隣接する$\alpha$炭素から強く電子を求引しているのが分かります(ちょうど真ん中あたりが青くなっていますよね?)。
また、一番右側の水素の部分はプロピオン酸分子の中で最も青いことから、最も電子密度が低い場所であることが分かります。このことから、カルボキシ基の水素は水などの極性溶媒中で容易に求核攻撃されるため脱プロトン化しやすく、プロピオン酸が酸性を示すことが納得できます。
また、例えばインジゴの電子密度は次のようになります。
インジゴでは2つの分子内水素結合を形成することが知られていますが、このように電子密度を見たら、より納得しやすくなるのではないでしょうか。
このように、分子の電子密度を視覚的に捉えることができれば、反応の進みやすさや原理がより深く理解できるようになります。有機化学では、このような量子力学・計算化学の結果を用いて反応機構の裏付けを行っていくことができるのです。
§ MolView on ウェブサイト
さらに、MolViewの出力結果の3Dモデルは、何とウェブページなどに直接埋め込むことができるのです。これはMolViewの最大の魅力と言えるかもしれません。MolViewはJavaで開発されていますので、このような動的な出力が得意なのです。
というわけで、以下にインジゴの3Dモデルを掲載します。これはマウスのドラッグなどで自由に動かせます。スマートフォンの場合はスライドすれば動かせます。回転操作も自由自在、縮小拡大も自由自在!
図18.インジゴの3Dモデル
(画像を触って動かしてみよう!)
さすがに結合をちぎったり折り曲げたりすることはできません(笑)が、構造を立体的に観察できるので、化合物を空間的に把握するツールとしてはこの上なく便利です。
さらに、MolViewでは有機化合物だけでなく、$\text{NaCl}$といった結晶や、ヘモグロビンなどのタンパク質まで調べることができます。
図19.塩化ナトリウムの3Dモデル
(画像を触って動かしてみよう!)
図20.ヘモグロビンの3Dモデル
(画像を触って動かしてみよう!)
いかがですか?なかなか面白いと思いませんか?
この他にも「Tools」のメニューから「Chemical data」の「Information ⅽard」を選べば化合物に関する情報が取得できますし、「Spectroscopy」を選べばMSスペクトルやIRスペクトルなども見ることができます。なんて贅沢な機能なのでしょうか!
こうした体験をインターネット上で、しかも無料でできてしまうというのだから伊達に世の中も進歩してないですよね(笑)。このMolViewが皆さんの化学の学習の一助となれば幸いです。運営している方に感謝してどんどん利用しましょう!
(2018/07/15追記)
ここまで説明しておいてアレですが、MolViewで実際の分子の再安定構造を再現できるとは限らないことは留意してください。例えば、ビフェニルの場合、中央のC-C結合に関するフェニル基同士の二面角は45°より少し小さいくらいなのですが、MolViewで表示させると2つのフェニル基が完全に直交してしまいます。ですので、3D表示させる際はあくまでも遊びで使う範囲に留めておきましょう(もし正確な安定構造を調べたいのであればキチンと量子化学計算を行う必要があります)。

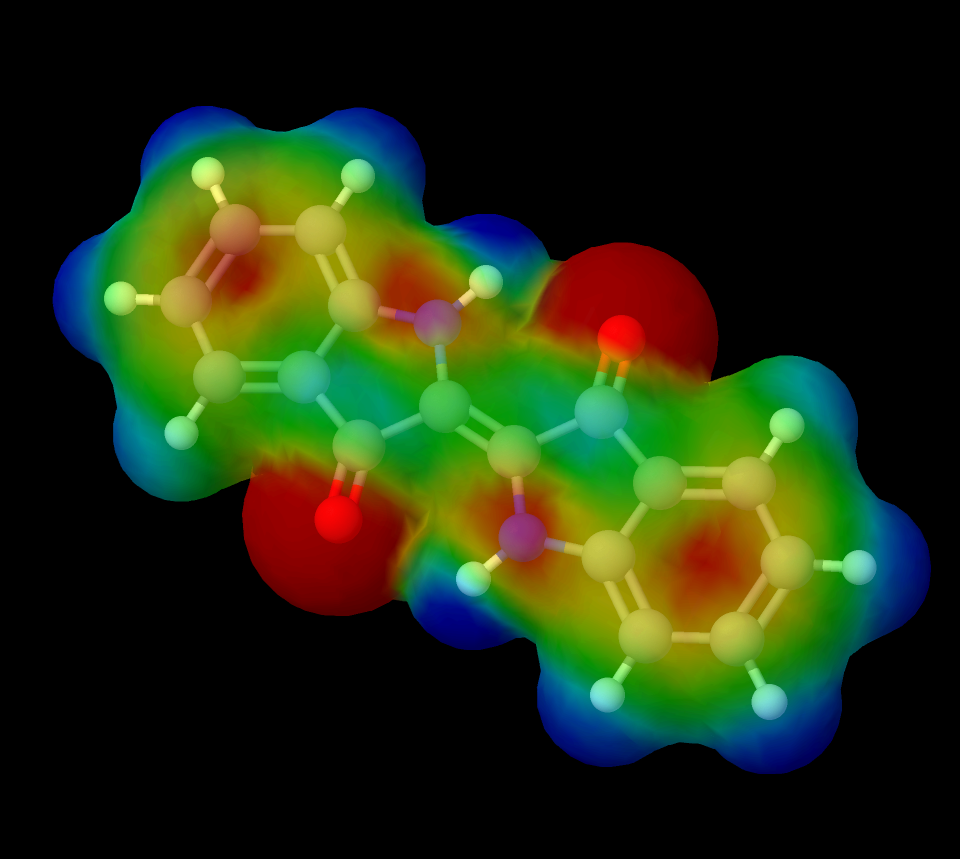
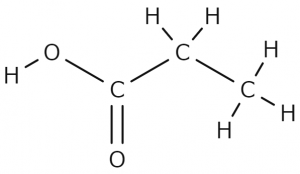 図1.プロピオン酸の構造式①
図1.プロピオン酸の構造式①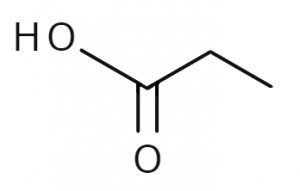
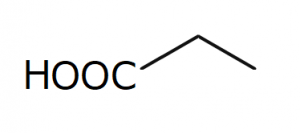
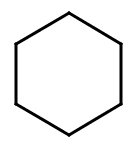 図4.シクロヘキサンの構造式
図4.シクロヘキサンの構造式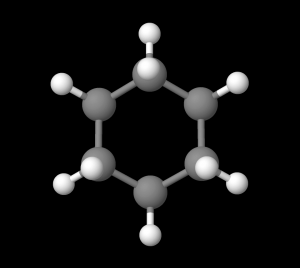 図5.シクロヘキサン(上から)
図5.シクロヘキサン(上から)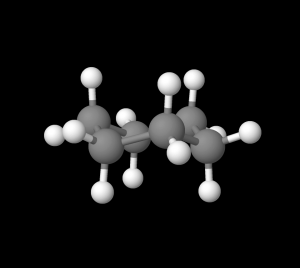 図6.シクロヘキサン(横から)
図6.シクロヘキサン(横から)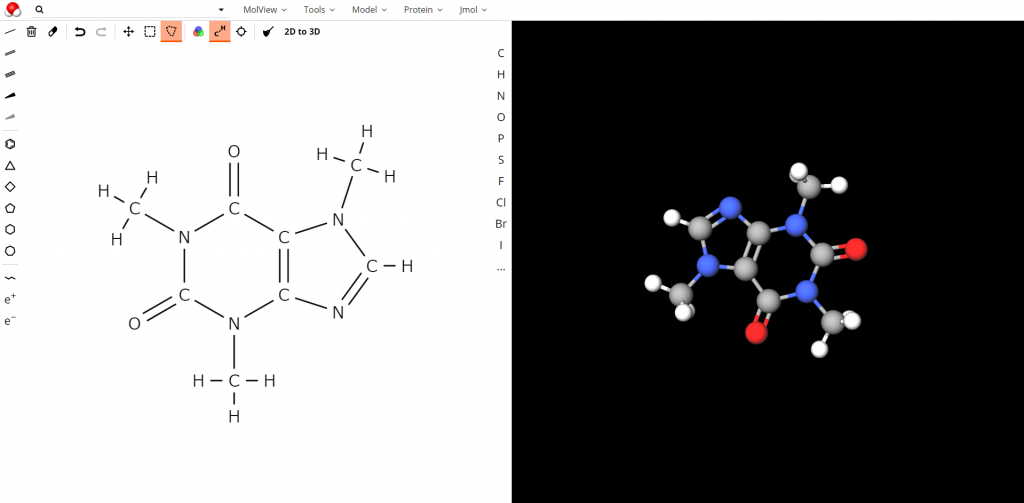 図7.編集画面
図7.編集画面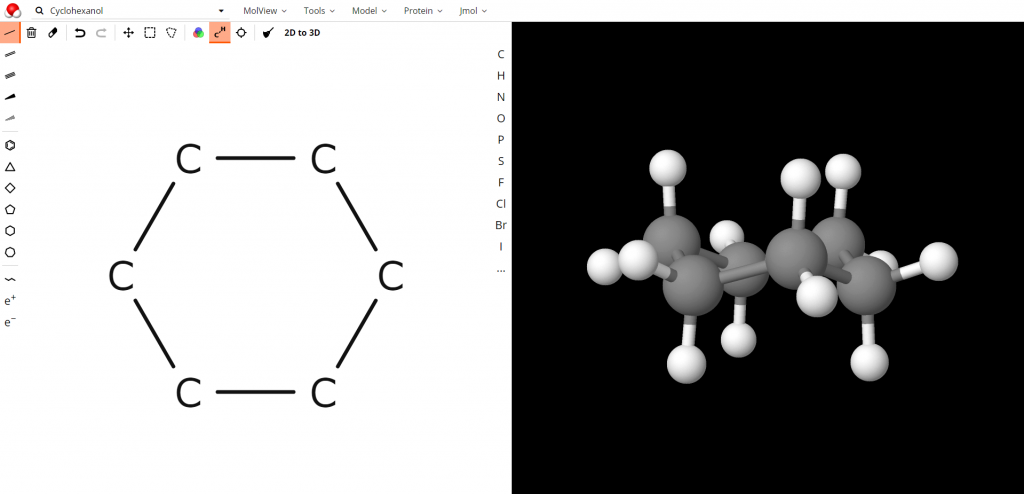 図8.編集画面(シクロヘキサンを例に)
図8.編集画面(シクロヘキサンを例に)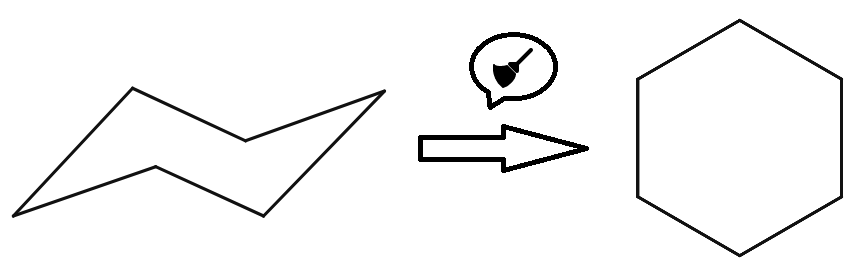 図9.クリーン機能
図9.クリーン機能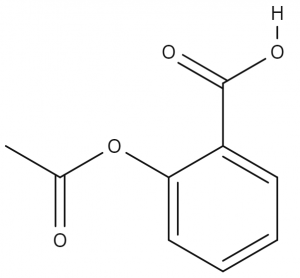 図10.アセチルサリチル酸の構造式
図10.アセチルサリチル酸の構造式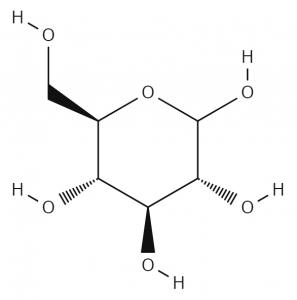 図11.D-グルコースの構造式
図11.D-グルコースの構造式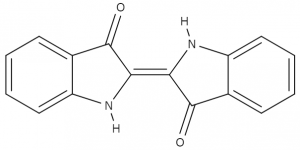 図12.インジゴの構造式
図12.インジゴの構造式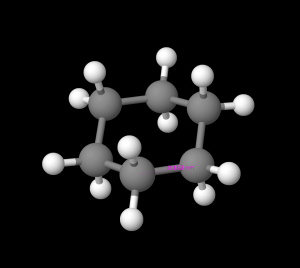

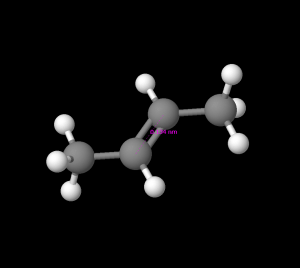
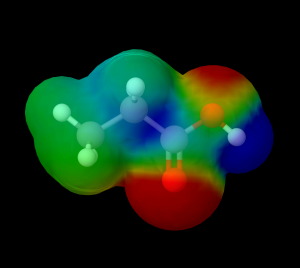 図16.プロピオン酸の電子密度状態
図16.プロピオン酸の電子密度状態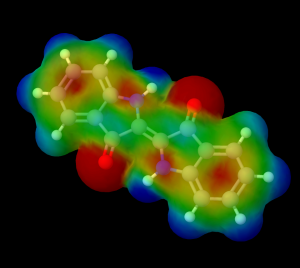
“オンラインで3Dの化学を遊ぶ” への1件の返信